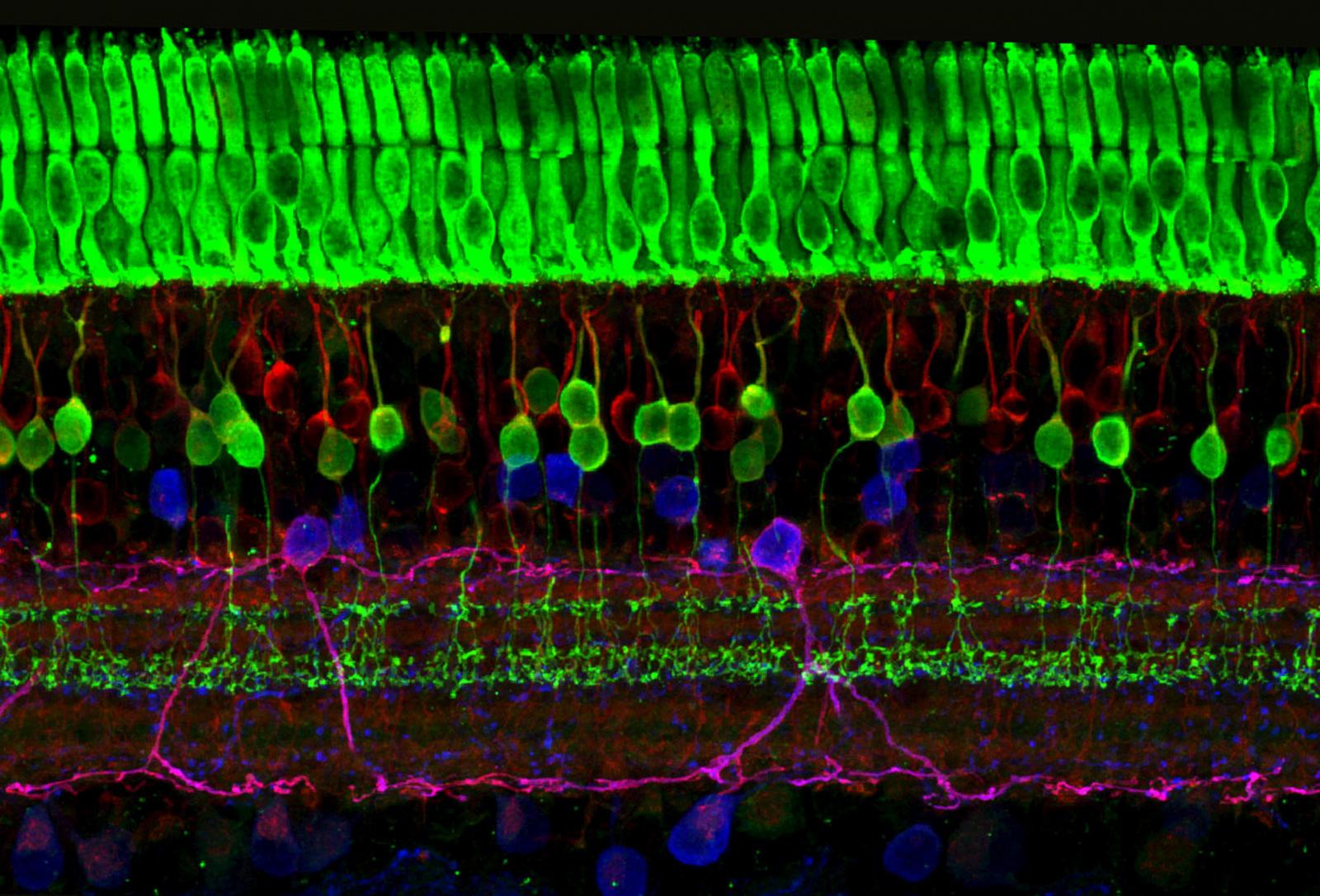
视网膜结构分区细胞数目统计比较
本文介绍在绘制完鸟类视网膜结构分区细胞数目/比例统计后(数据储存在 meta_info.txt 中),进行物种之间的比较。 以银鸥(Larus argentatus)和鸬鹚(Phalacrocorax carbo)为例,可用如下代码提取、合并 meta_info 的信息,并绘制多物种视网膜中央区与旁区细胞数目的统计图进行比较: 1234567891011121314151617181920212223242526272829303132333435363738394041424344454647484950515253545556575859606162636465666768library(ggplot2)library(dplyr)library(ggforce)library(tidyr)library(ggsci)merge_meta <- function(df, species_name){ df %>% mutate( species = species_name, comparison_...
A brief note on parity violation
I. Weak Nuclear ForceThere are four fundamental interactions in nature — gravitational force, electromagnetic force, strong nuclear force and weak nuclear force. Weak nuclear force (also called “weak interaction”) is the mechanism of interaction between subatomic particles (particles smaller than atoms) responsible for the radioactive decay of atoms, which participates in nuclear fission and fusion. Different from the other three interactions, the weak force is transmitted through exchanging...
h5ad 文件转 rds 文件
在单细胞测序数据分析中,常见的数据文件格式有 h5ad(AnnData 格式)和 rds(R 数据格式).前者主要用于 Python 环境下的单细胞数据处理(如 scanpy),而后者则应用于 R 语言环境中(如 Seurat).本文将结合我进行的单细胞注释分析,介绍如何将 h5ad 文件转换为 rds 文件,以便在 R 环境中进行后续分析. 数据准备与转换工作假设我们在 Python 环境下做完细胞注释后的单细胞数据保存为 adata.h5ad 文件,里面保存有细胞的表达矩阵、注释信息等.但后续我们需要在 R 环境中使用 Seurat 包进行进一步分析,因此需要将该文件转换为 rds 格式。转换使用的工具为 sceasy 这个 R package.具体代码如下: 1234567891011121314library(sceasy)library(reticulate)loompy <- reticulate::import('loompy')# 读取 h5ad 文件并转换为 rds 文件h5ad_file = "adata.h5ad"...
动态系统稳定性与 Lotka-Volterra 模型浅略研究
稳定性理论(Stability theory)简介稳定性理论研究微分方程的解及动态系统的轨迹在初始条件有微小扰动时的稳定性.在某初始平衡条件(Equilibrium)下,给系统向某一方向施加一微小扰动,若系统最终可能偏离平衡状态而无法回到原始位置,则该平衡点是不稳定的.反之,若为稳定平衡点,则最终能回到原始位置,如摆线的振荡、阻尼振子等系统. 衰减的阻尼正弦波.来自:Wikipedia. 稳定性的判断动态系统可用微分方程来描述.对于一维的常微分方程如 $\frac{dx}{dt} = f(x)$,其平衡点 ${x^*}$ 满足 $f(x^\ast) = 0$.若 $f’(x^\ast) < 0$,则平衡点是稳定的;若 $f’(x^\ast) > 0$,则平衡点是不稳定的.值得注意的是,若 $f’(x^\ast) = 0$(如下图第二个 stable 处),则需要其他方法判断稳定性. 一维动态系统的稳定性判断. 而对于二维系统 $\frac{d{x_1}}{dt} = f_1(x_1...
构建 SAW 分析参考索引
在运行 SAW (Stereo-seq Analysis Workflow) count 分析前,需要先生成参考基因组索引 (index).这一步可以由 SAW makeRef 流程分析实现.我们需要提供的输入文件为参考基因组序列 reference.fna 和对应的注释文件 reference.gff/gtf. miniprot 基因注释由于原先的参考基因组 Larus_argentatus.fna 并未注释出关键的三个视蛋白 (Opsins) 基因 OPN1SW、OPN2SW 与 OPN1LW,因此需要重新对参考基因组进行注释,选用的软件为 miniprot,具体注释方法在此不展开论述.最终只注释出位于 Chr1 的 OPN2SW 基因,需要添加的另外两个基因序列所在染色体分别为 CAYQHM010000238.1.fna 和 OZ207386.1.fna,miniprot 注释输出的 GFF3 格式文件分别为 CAYQHM010000238.1.gff 和 OZ207386.1.gff. 注释文件格式转换原先的基因组注释文件为 .gtf 格式,因此需将 CAYQHM0100...
Hello World
Welcome to Hexo! This is your very first post. Check documentation for more info. If you get any problems when using Hexo, you can find the answer in troubleshooting or you can ask me on GitHub. Quick StartCreate a new post1$ hexo new "My New Post" More info: Writing Run server1$ hexo server More info: Server Generate static files1$ hexo generate More info: Generating Deploy to remote sites1$ hexo deploy More info: Deployment